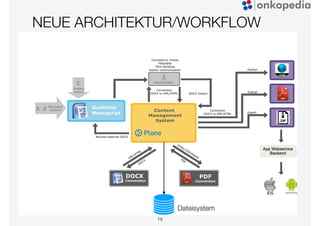
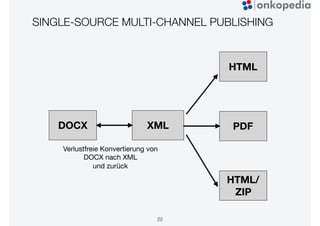
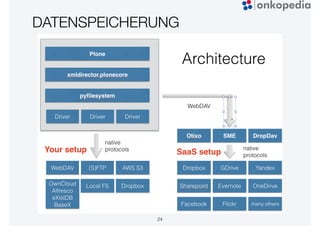
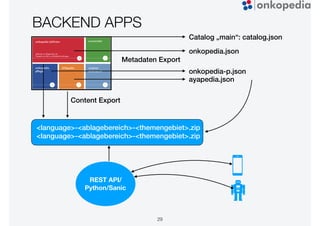
Das Dokument beschreibt die Entwicklung von Onkopedia, einem Leitlinienportal für die Hämatologie und Onkologie, das seit 10 Jahren besteht. Es wird die technische Evolution von Onkopedia von Version 1.0 bis 4.0 sowie geplante zukünftige Entwicklungen wie Onkopedia 5.0 besprochen, darunter die Einführung von Apps und neuen Suchfunktionen. Onkopedia dient als Informationsquelle für Mediziner, Patienten und Kostenträger und hat sich zu einem bedeutenden und renommierten Werkzeug im Bereich der evidenzbasierten Medizin entwickelt.