Tema 9 mensaje genético
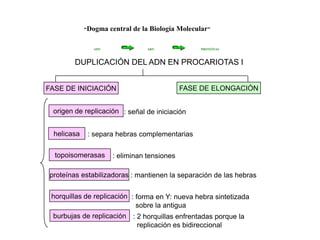
- 1. “Dogma central de la Biología Molecular" ADN ARN PROTEÍNAS DUPLICACIÓN DEL ADN EN PROCARIOTAS I FASE DE INICIACIÓN FASE DE ELONGACIÓN origen de replicación : señal de iniciación helicasa : separa hebras complementarias topoisomerasas : eliminan tensiones proteínas estabilizadoras : mantienen la separación de las hebras horquillas de replicación : forma en Y: nueva hebra sintetizada sobre la antigua burbujas de replicación : 2 horquillas enfrentadas porque la replicación es bidireccional
- 2. DUPLICACIÓN DEL ADN EN PROCARIOTAS II FASE DE INICIACIÓN FASE DE ELONGACIÓN primasa: ARNpolimerasa : sintetiza ARN que actúa de CEBADOR ADNpolimerasa III : sintetiza la HEBRA CONDUCTORA a partir del cebador (5´ →3´) fragmentos de Okazaki : sintetizados sobre la HEBRA RETARDADA ADNpolimerasa I : retira nucleótidos de ARN y añade de ADN ADNligasa : une los fragmentos de ADN sintetizados
- 3. DUPLICACIÓN DEL ADN EN EUCARIOTAS parecida a la de procariotas aunque con algunas diferencias las histonas se duplican durante la replicación origen de replicación : se inicia de manera simultánea en un centenar de puntos llamados REPLICONES fragmentos de Okazaki : menores proceso más lento por la presencia de histonas ocurre durante el período S de la interfase
- 4. TRANSCRIPCIÓN EN PROCARIOTAS INICIACIÓN ELONGACIÓN FINALIZACIÓN MADURACIÓN promotor : región del ADN que no se transcribe que determina la hebra de ADN que se transcribe secuencias de : nucleótidos del promotor consenso INICIACIÓN ARN polimerasa : se fija al promotor, desenrolla una vuelta de hélice hebra patrón : hebra del ADN que se transcribe ELONGACIÓN :síntesis de ARN en dirección 5´ →3´ por la ARNpolimerasa FINALIZACIÓN : terminador : región del ADN que forma un bucle en el ARN y favorece la separación y la formación de la doble hélice de ADN MADURACIÓN : transcrito primario :ARNt y el ARNr sufren maduración (rotura y : empalme)
- 5. TRANSCRIPCIÓN EN EUCARIOTAS parecida a la de procariotas aunque con algunas diferencias hay 3 tipos de ARN polimerasas maduración: eliminación de INTRONES y empalme de EXONES ADN asociado a histonas
- 6. TRANSCRIPCIÓN DE ARNm EN EUCARIOTAS INICIACIÓN ELONGACIÓN FINALIZACIÓN MADURACIÓN secuencias de : 2, CAAT y TATA (la más frecuente) consenso INICIACIÓN factores de iniciación : proteínas que se tienen que fijar a las de la transcripción secuencias de consenso para iniciar ELONGACIÓN : capucha : metil-guanosina-triP en extremo 5´ terminador : secuencia TTATTT FINALIZACIÓN cola de poliA : 200 A en extremo 3´ MADURACIÓN : transcrito primario : separación de intrones y empalme de exones : por ligasas
- 8. EL CÓDIGO GENÉTICO correspondencia entre los tripletes de nucleótidos del ARNm y los aa que forman las proteínas hay 64 tripletes para 20 aa varios tripletes codifican para el mismo aa tripletes de fin de traducción: UAA, UAG, UGA triplete señal de inicio: AUG (metionina) degeneración del código genético: algunos aa están codificados por varios tripletes distintos
- 9. TRADUCCIÓN síntesis de la secuencia de aa de una proteína siguiendo el mensaje genético del ARNm ACTIVACIÓN DE LOS aa TRADUCCIÓN ATP AMP + PPi aa + ARNt aminoacil-ARNt aminoacil-ARNt-sintetasa con el aa unido al extremo 3´del ARNt INICIACIÓN ELONGACIÓN FINALIZACIÓN
- 10. INICIACIÓN DE LA TRADUCCIÓN codón de iniciación (AUG) del ARNm + subunidad menor del ribosoma + ARNt de metionina o formilmetionina (anticodón UAC) + subunidad mayor del ribosoma COMPLEJO RIBOSOMAL O ACTIVO CENTRO P O PEPTIDIL CENTRO A O ACEPTOR donde se sitúa el primer donde se sitúan los siguientes aminoacil-ARNt aminoacil-ARNt
- 11. ELONGACIÓN DE LA TRADUCCIÓN 1º centro P ocupado por ARNt con aa1 ENLACE PEPTÍDICO centro A ocupado por un 2º ARNt con un aa2 entre aa1 aa2 peptidil transferasa 2º centro P ocupado por ARNt sin aa ARNt sin aa sale del ribosoma translocación ribosomal ARN con aa1-aa2 queda en centro P centro A libre 3º llegada de un ARNt con aa3 al centro A repetición de otro ciclo de elongación